Wissenschaftler untersuchen 59 Tumor-Zelllinien
Typisches Proteinprofil von Tumorzellen entschlüsselt
In der bislang größten Studie dieser Art identifizierten Wissenschaftler der Technischen Universität München (TUM) über 10.000 verschiedene Proteine in Krebszellen. „Nahezu alle Tumormedikamente richten sich gegen zelluläre Proteine“, sagt Prof. Bernhard Küster, Leiter des TUM-Lehrstuhls für Proteomik und Bioanalytik. „Wenn das Proteom, also das Proteinportfolio von Tumorzellen bekannt ist, steigen die Chancen, neue Angriffspunkte für Medikamente zu finden.“
Die Wissenschaftler untersuchten 59 Tumor-Zelllinien des National Cancer Institute (USA). Die unter dem Etikett „NCI-60“ geführten Zelllinien repräsentieren die häufigsten Tumorerkrankungen in neun Geweben (z.B. Gehirn, Brust, Darm, Haut, Blut). Sie werden von Krebsforschern auf der ganzen Welt für ihre Versuche genutzt. TUM-Bioinformatiker Dr. Amin Gholami: „Bisher war das Proteom der NCI-60-Zelllinen weitgehend unbekannt – dabei sind es die Proteine, die den Unterschied zwischen einer gesunden und einer Tumorzelle ausmachen.“
Proteine in Tumorzellen: Viele Gemeinsamkeiten – große Vielfalt
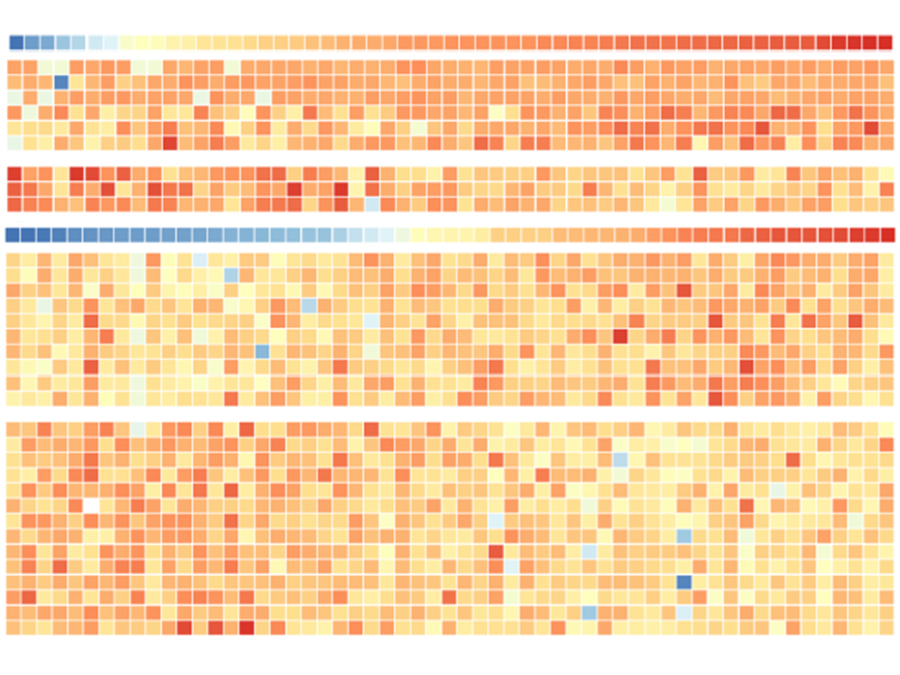
Die Wissenschaftler fanden mehr als 10.000 verschiedene Proteine in den NCI-60-Zelllinien. Über 5.000 davon kommen in unterschiedlicher Häufigkeit in Tumor-Zellinien aller Gewebearten vor. „Wir können davon ausgehen, dass es sich dabei um das Kernproteom von Krebs handelt“, so Küster. Zwischen den Tumorzellen verschiedener Gewebe zeigten sich aber auch klar unterscheidbare Proteinprofile – ein deutlicher Hinweis darauf, dass die Tumorzellen typische Eigenschaften gesunder Zellen des gleichen Gewebes aufweisen.
375 der rund 10.000 Proteine gehören zur Gruppe der Kinasen. Diese Proteine sind dafür zuständig, Signale weiterzuleiten, mit denen Zellen zum Beispiel ihren Stoffwechsel, die Zellteilung oder die Kommunikation mit anderen Zellen im Gewebe steuern. Die große Bandbreite verschiedener Kinasen im NCI-60-Bestand erklärt Tumorbiologe Dr. Zhixiang Wu so: „Anders als den gesunden Körperzellen stehen Tumorzellen viele Signalwege offen, um ihre Teilung zu aktivieren und ihr Überleben zu sichern.
Küster ergänzt: „Die Kinasen tragen dazu bei, dass Tumorzellen sich immer weiter vermehren. Ihre Vielfalt zeigt, wie unterschiedlich diese Mechanismen in menschlichen Krebserkrankungen sind – eine bedeutende Erkenntnis für die personalisierte Medizin.“
Wirksamkeit von Medikamenten abhängig vom Proteinmuster
Außerdem konnten die TUM-Forscher erstmals belegen, dass es vom Proteinmuster der Zellen abhängt, wie gut Krebsmedikamente wirken. „Wir haben untersucht, wie die Zelllinien auf insgesamt 108 verschiedene Krebsmedikamente reagieren. Tatsächlich gibt es Proteine, die Auskunft geben, ob eine Zelle auf bestimmte Therapeutika anspricht – oder resistent dagegen ist“, sagt Dr. Hannes Hahne, TUM-Experte für massenspektrometrische Verfahren. Als Beispiel nennt er das Protein 14-3-3 zeta/delta, das im Verdacht steht, Resistenzen gegen Krebsmedikamente zu vermitteln.
Die NCI-60-Proteom-Daten können Wissenschaftler in einer Datenbank abrufen. „Wir wollen damit einen Beitrag leisten, die Proteom-Forschung auf dem Gebiet von Krebserkrankungen weiter voranzubringen“, resümiert Küster. „Als nächstes werden wir das Proteom der ‚Cancer Cell Line Encyclopedia’ in Angriff nehmen, mit denen Pharmafirmen Wirkstoffe gegen Krebs testen.“
Publikation:
Global proteome analysis of the NCI-60 cell line panel; Amin Moghaddas Gholami, Hannes Hahne, Zhixiang Wu, Florian Johann Auer, Chen Meng, Mathias Wilhelm and Bernhard Kuster, Cell Reports Volume 4, 2013, doi: 10.1016/j.celrep.2013.07.018
Links:
Kontakt:
Technische Universität München
Lehrstuhl für Proteomik und Bioanalytik
Prof. Dr. Bernhard Küster
T: +49 8161 71-5697
E: kuster@tum.de
W: www.weihenstephan.de/bt/
Technische Universität München
Corporate Communications Center
- Barbara Wankerl
- barbara.wankerl@tum.de
- presse@tum.de
- Teamwebsite